2. Analiza podobieństwa genetycznego.
Do analizy podobieństwa genetycznego wyselekcjonowanych genotypów rabarbaru zastosowano markery mikrosatelitarne ISSR (ang. inter simple sequence repeat). Do badań wykorzystano 15 oligonukleotydów komplementarnych do sekwencji ISSR. Testy PCR-ISSR prowadzono w zoptymalizowanych warunkach termicznych reakcji amplifikacji na matrycach DNA badanych genotypów rabarbaru. Uzyskane produkty amplifikacji rozdzielano przez elektroforezę w żelach agarozowych, a następnie przeprowadzono analizę porównawczą wzorów prążkowych dla poszczególnych genotypów. Na podstawie oceny obecności lub braku poszczególnych produktów reakcji ISSR-PCR opracowano macierz podobieństwa genetycznego, podobieństwo genetyczne pomiędzy parami wszystkich genotypów obliczano zgodnie z formułą Dice’a. W oparciu o matrycę opracowano drzewo filogenetyczne badanych genotypów za pomocą analizy skupień metodą UPGMA (unweighted pair group method with arithmetic average) z zastosowaniem programu XLSTAT (Addinsoft 2016).
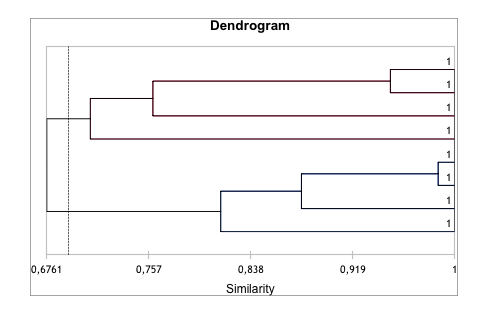
Analiza podobieństwa genetycznego badanych genotypów rabarbaru umożliwiła wyodrębnienie dwóch głównych grup (klastrów), w jednej znalazły się genotypy L1, L2, L3 i L4, w drugiej zaś genotypy M1, M2, M3 i G (rys. 1). Największe podobieństwo genetyczne występuje pomiędzy genotypami M1 i M2 (99%) oraz L1 i L2 (95%). Wykazano także duże podobieństwo genetyczne odmiany Goliath do genotypów z grupy Malinowy. Podobieństwo genetyczne pomiędzy głównymi klastrami wynosiło 68%.